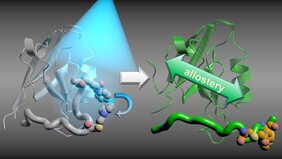
Das kann durch gezielt dafür designte Moleküle erreicht werden, die dadurch pharmakologische Wirkung als Schmerzmittel oder Chemotherapeutikum erhalten. Um solche Moleküle zu bauen, müssen Wissenschaftlerinnen und Wissenschaftler die möglichen Mechanismen von Allosterie kennen. Ein Team um Prof. Dr. Gerhard Stock aus der Arbeitsgruppe Biomolekulare Dynamik am Physikalischen Institut der Universität Freiburg und Prof. Dr. Peter Hamm vom Institut für Chemie der Universität Zürich/Schweiz liefern in der Fachzeitschrift PNAS dafür wichtige Einblicke.
Die Forschenden haben zeitaufgelöst allosterische Veränderungen im Testprotein PDZ2 verfolgt, die durch die Bindung eines so genannten Liganden hervorgerufen werden – also eines Stoffes, der in der Lage ist, an ein Zielprotein anzudocken. Die Arbeitsgruppe der Universität Zürich führte hierzu zeitaufgelöste Vibrationsspektroskopie durch, die Physikerinnen und Physiker der Albert-Ludwigs-Universität simulierten am Tübinger Großrechner BinAC die entsprechenden Veränderungen auf atomistischer Ebene. Durch diese Kombination konnten die Wissenschaftler mit atomarer Auflösung und einem Zeitskalenbereich von Pico- bis Mikrosekunden nachvollziehen, wie eine Veränderung des Ligandenbindungsmodus durch das Protein läuft. Diese Echtzeitbeobachtung der Signalübertragung in Proteinen zeigte: Grundlage der Allosterie sind die Veränderungen sowohl der Struktur als auch der Dynamik des Proteins, die über hierarchische Zeitskalen verläuft. Deshalb braucht eine strukturelle Veränderung in etwa zehnmal länger als eine ihr vorangehende Veränderung.
Albert-Ludwigs-Universität Freiburg
Originalpublikation:
Bozovic, O., Zanobini, C., Gulzar, A., Jankovic, B., Buhrke, D., Post, M., Wolf, S., Stock, G., Hamm, P. (2020): Real-time observation of ligand-induced allosteric transitions in a PDZ domain. In: PNAS. DOI: 10.1073/pnas.2012999117