Archaeen vereinen bakterielle und eukaryotische Merkmale. Sie haben aber auch einzigartige Eigenschaften und regulatorische Merkmale, und sind damit ein wichtiges Untersuchungsobjekt von fundamentaler Bedeutung.
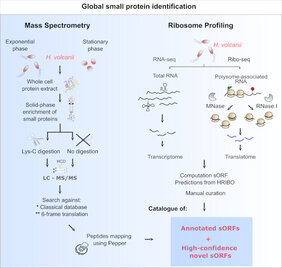
In einem multidisziplinären Ansatz haben die Gruppen von Anita Marchfelder (Universität Ulm), Cynthia Sharma (Universität Würzburg), Dörte Becher (Universität Greifswald) und Rolf Backofen (Universität Freiburg) nun das „kleine Proteom“ des Modell-Archeons Haloferax volcanii analysiert.
Dazu wurde Massenspektrometrie (MS) für kleine Proteine optimiert und mit Ribosome-Profiling (Ribo-seq) kombiniert. Bei Ribo-seq werden ausschließlich RNAs sequenziert, die mit Ribosomen assoziiert sind und somit translatiert werden. Verbunden mit einer sorgfältigen Bioinformatik erlaubt dieser Ansatz bisher nicht annotierte Proteine zu finden und sicher zu sein, dass die gefundenen offenen Leserahmen tatsächlich für die Proteinsynthese genutzt werden.
Diese erste Multi-Omics-Analyse eines archaealen kleinen Proteoms zeigt, dass 2/3 der annotierten kleinen Proteine unter Standardwachstumsbedingungen exprimiert werden, und dass es zusätzlich 47 bisher nicht identifizierte Gene für kleine Proteine gibt.
Die genauere Untersuchung des lange vernachlässigten „kleinen Proteoms“ wird sicher noch einige Überraschungen bieten, vor allem aber einen vollständigeren Einblick in die biochemischen Leistungen der Archaeen gebe.
Universität Ulm
Originalpublikation:
Lydia Hadjeras, Jürgen Bartel, Lisa-Katharina Maier, Sandra Maaß, Verena Vogel, Sarah L Svensson, Florian Eggenhofer, Rick Gelhausen, Teresa Müller, Omer S Alkhnbashi, Rolf Backofen, Dörte Becher, Cynthia M Sharma, Anita Marchfelder, Revealing the small proteome of Haloferax volcanii by combining ribosome profiling and small-protein optimized mass spectrometry, microLife, Volume 4, 2023, uqad001, https://doi.org/10.1093/femsml/uqad001